结直肠癌相关的T细胞受体库异常与肠道微生物组转移和体细胞突变有关
公司新闻
2024-09-06 10:42:11
### **背景**
大肠癌,作为全球范围内高发的癌症之一,其复杂的病因一直困扰着医学界。近年来,科学研究逐渐揭示了肠道微生物群与大肠癌之间的神秘联系。肠道微生物群不仅参与日常的消化过程,更是影响着我们的免疫系统功能。
与许多疾病一样,结直肠癌(CRC)的肿瘤形成是多因素的,涉及免疫、环境因素和各种促进疾病发展的遗传因素。越来越多的证据表明,肠道微生物组与结直肠癌的发生和发展有关,这些微生物对免疫成熟很重要。然而,目前还缺乏整合CRC患者微生物谱、T细胞受体(TCR)和体细胞突变的系统视角。
### **方法**
通过高通量测序分析CRC患者(n = 107)和健康供者(n = 30)外周血中表达的TCRβ谱的特征;宏基因组测序检测CRC患者(n = 97)与HC健康供者(n = 30)核梭杆菌、大肠杆菌和Dasheen花叶病毒prausnitzii粪杆菌和Roseburia intestinal丰度,分析两组之前的差异。构建了一个基于微生物组和TCR库的随机森林分类器(包含15个特征),该分类器可作为筛查CRC患者的临床检测方法。
### **结果**
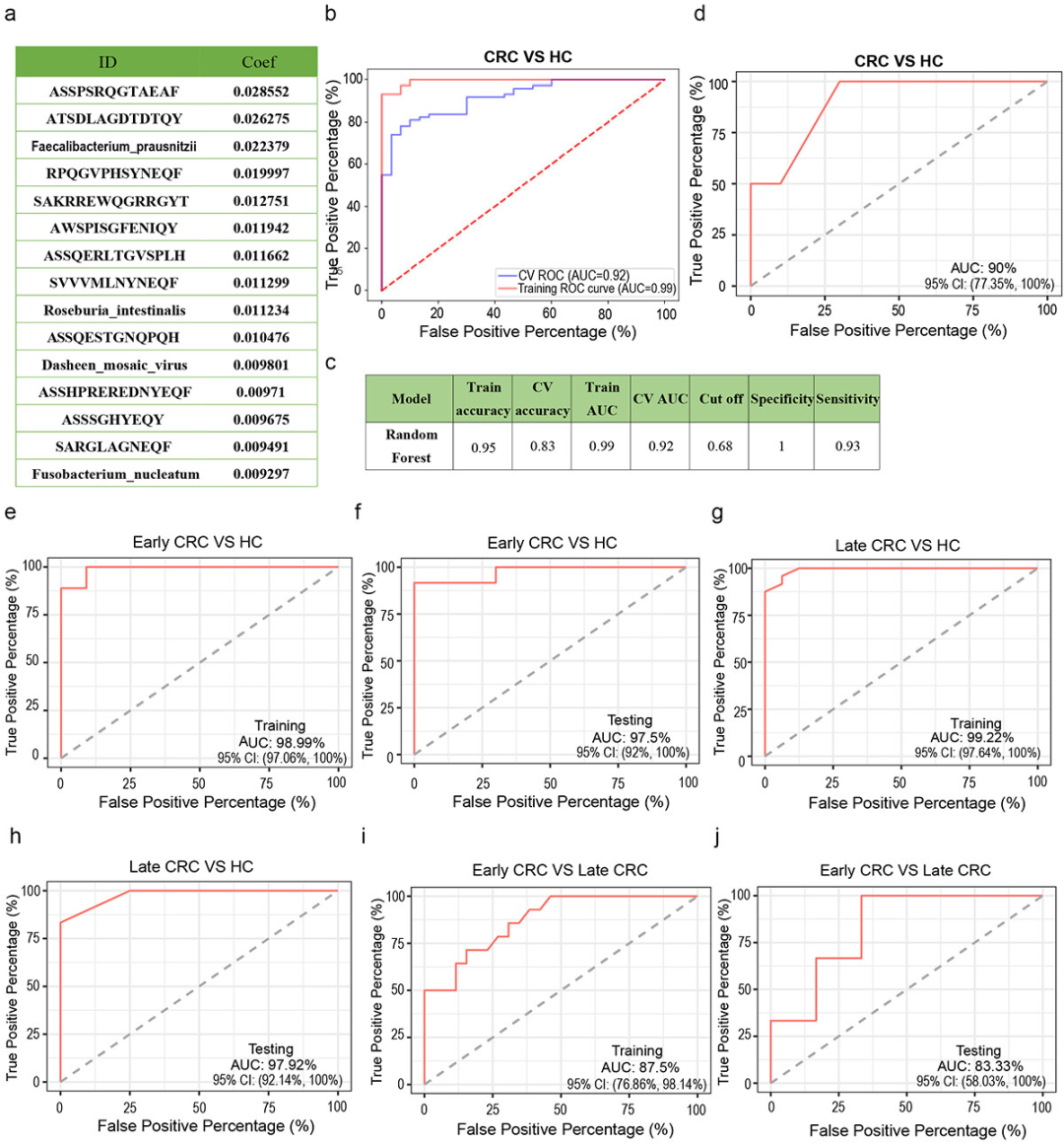
**1、结直肠癌患者和HC个体在CDR3区域的Vβ和Jβ基因使用上存在差异。**
(a)健康供体6个代表性库的V-J基因使用组合。x轴和y轴分别描绘了功能性人 类TRBV和TRBJ等位基因。z轴是给定V-J组合的TCRβ序列的计数(注意z轴的尺度根据最大计数的变化而变化)。(b) 6种CRC患者代表性曲目的V-J基因使用组合。(c) Vβ基因使用比较。x轴表示所有功能性人类TRBV等位基因,y轴表示使用每个TRBV等位基因的健康供体或结直肠癌患者的所有基因库中TCRβ序列的百分比。(注:图a、b、c、d由益安博助力绘制)

**2、结直肠癌患者和健康供者TCR谱特异性序列特征**
(a)健康对照组与结直肠癌患者HEC数量分布比较。(b)各组内克隆型重叠。(c) TCRβ CDR3氨基酸序列长度分布比较。y轴为具有相应CDR3长度的TCRβ CDR3克隆类型的百分比。(d) CRC特异性序列图。直方图中显示了前50个CRC特异性CDR3序列,表中为CRC-spec最高的10个序列。(e)所有样本的CDR3序列热图。(注:图a、b、c、d、e由益安博助力绘制)
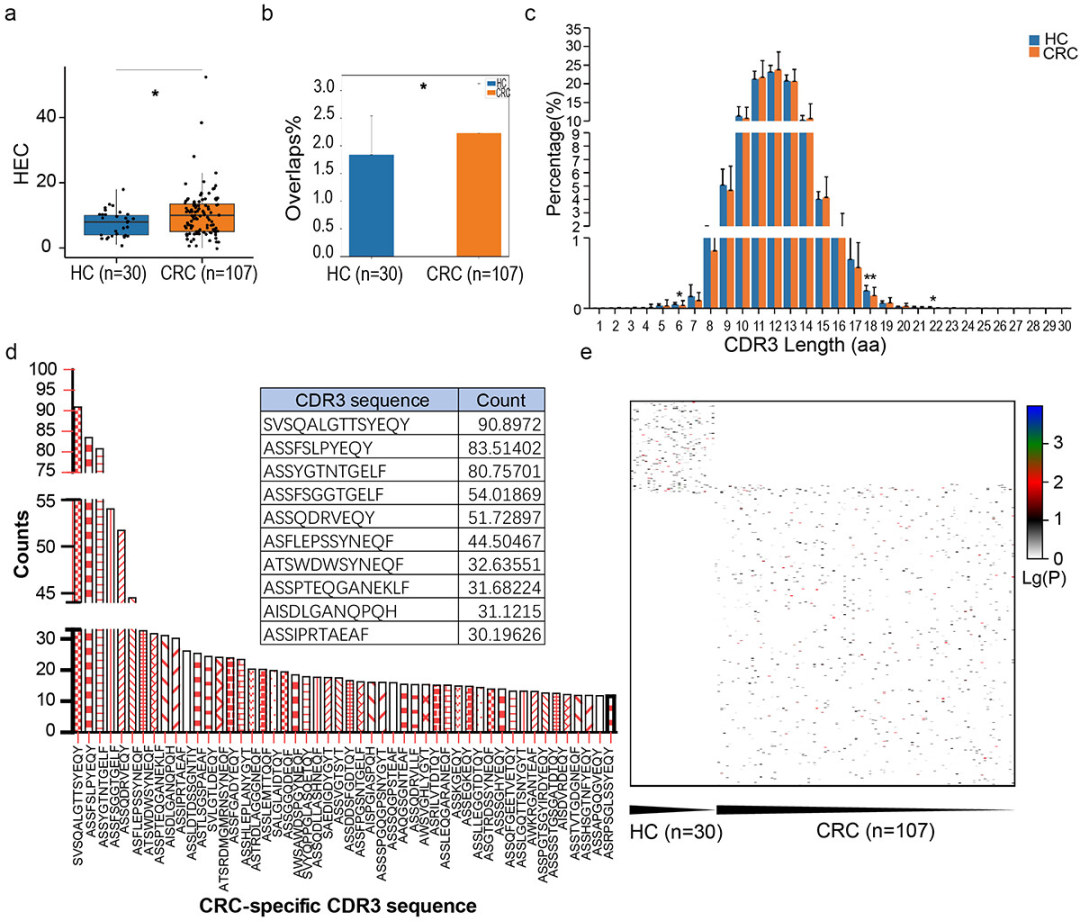
**3、HC个体和CRC患者肠道微生物群的概况。**
a) 每个样本中相对表达丰度排名前九的物种。(b) CRC组的Shannon多样性指数显著高于对照组。(c) NMDS显示CRC患者和HC对照之间整体粪便微生物组成存在差异。(d) 微生物群落的物种丰度分析,分类进化图展示了同源组(物种丰度大于或等于0.5%)中所有分支的信息。圆圈大小代表物种丰度占比,颜色代表最丰富类群的相对富集程度。(e) lefse图显示LDA得分大于预设值的显著差异物种;默认得分为2.0。柱状图的长度代表LDA得分(不同组间显著差异物种的影响程度)。(f, g) CRC患者和HC对照之间显著差异表达基因。(h)利用GO数据库和功能组进行途径富集分析,根据差异表达基因对前30个富集GO术语进行分组。低FDR-p值用红色表示,高FDR-p值用绿色表示;圆圈的大小与富集基因的数量成正比。(注:图b由益安博助力绘制)
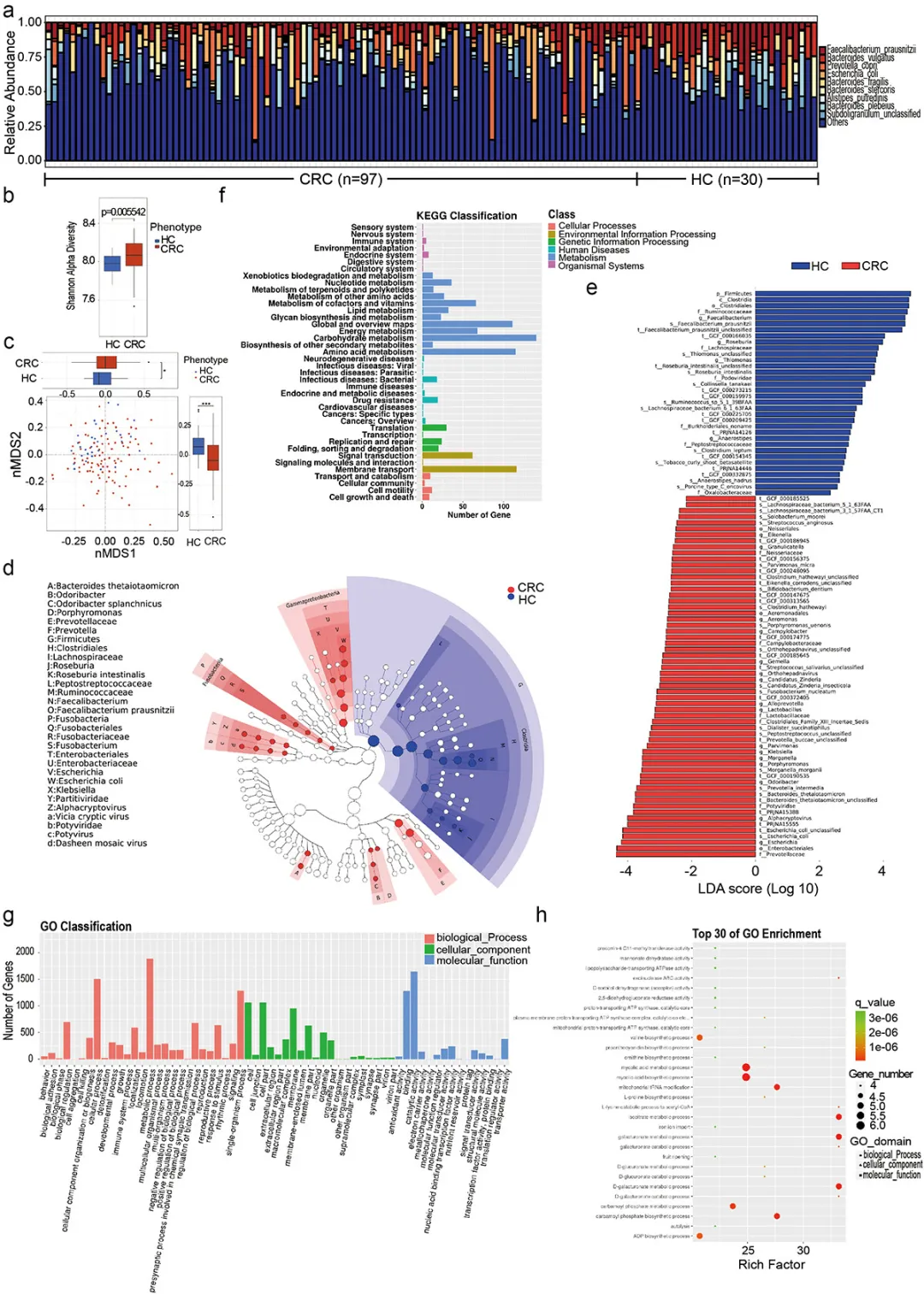
**4、CRC相关的体细胞突变与TCR和肠道微生物组有关。**
(a) CRC样本突变谱图。瀑布图显示了每个样本中每个基因的突变信息,其中底部带有注释的各种颜色代表了不同的突变类型。图例上方的条形图显示了突变负担。(b)统计计算的突变信息摘要。根据不同的类别对突变类型进行分类,其中错义突变占比最大,SNP出现频率高于插入或缺失,且SNV以C>T最为常见;特定样本的肿瘤突变负荷;结直肠癌十大突变基因;不同功能类型SNV/InDel位点的分布比例;所有样本的InDel插入/删除长度分布;横坐标表示插入(>0)和删除(<0)片段的长度,纵坐标表示对应的InDel比。(c) 16个目标基因与不同微生物之间的相关性。(d) 16个靶基因与TCR CDR3序列的相关性。(注:图d由益安博助力绘制)
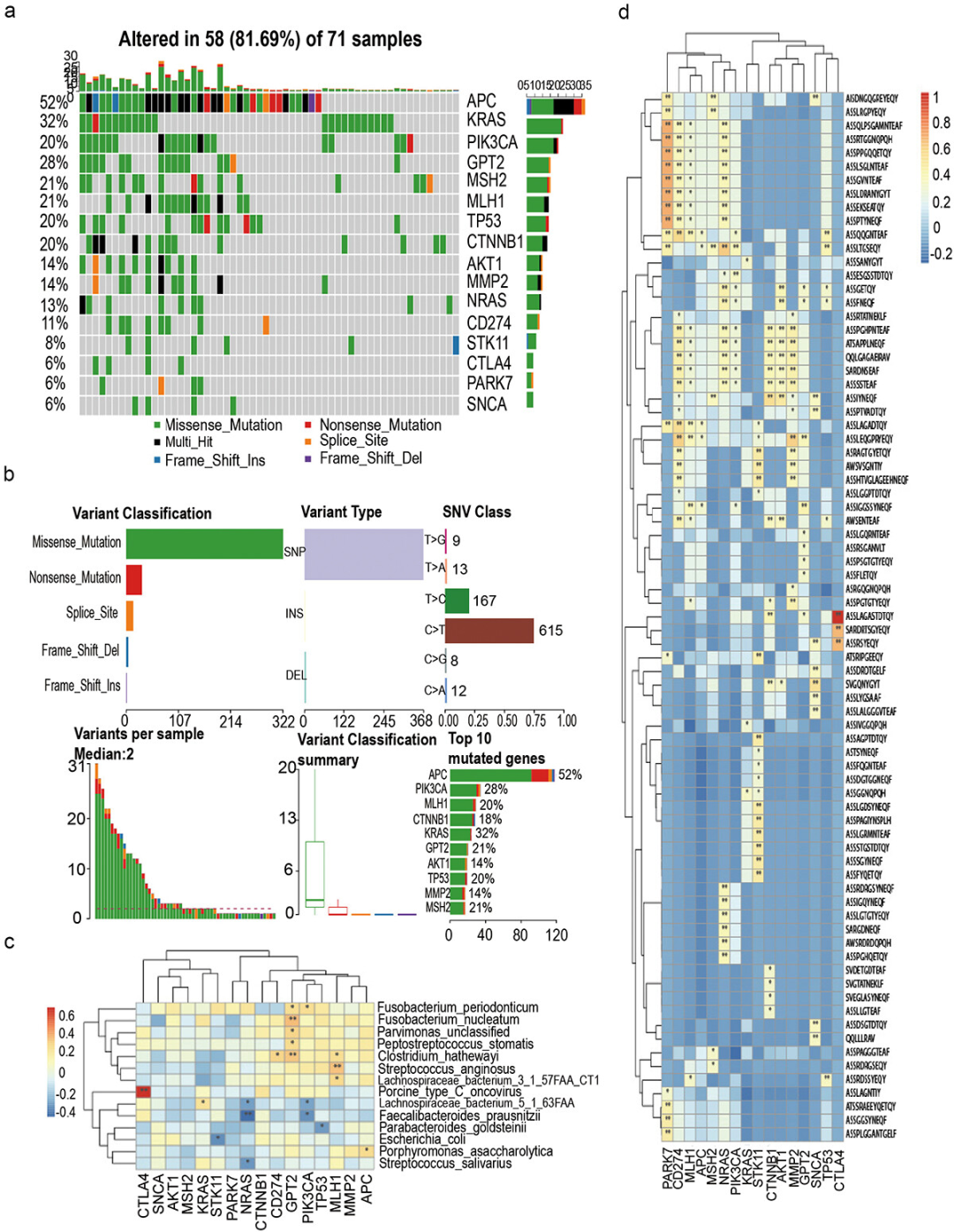
**5、基于肠道微生物谱和TCR谱建立CRC患者与HC个体的预测分类器。**
(a)基于微生物组和TCR库的随机森林分类器的15个特征。15个指标的特征重要性排序系数值如图5a所示。(b-c)随机森林算法构建的ROC曲线。基于AUC可以评估最终模型的效果。(d)经过训练的随机森林模型在验证队列上的AUC为0.90。(e, f)生物标志物对健康个体早期结直肠癌的诊断较好,训练AUC和检测AUC分别为98.99%和97.5%。(g, h)生物标志物对健康个体晚期结直肠癌的诊断效果也较好,训练AUC和测试AUC分别为99.22%和97.92%。(i, j)生物标志物在区分不同阶段CRC方面表现稍差,训练和测试AUC分别为87.5%和83.33%。(注:图a由益安博助力绘制)
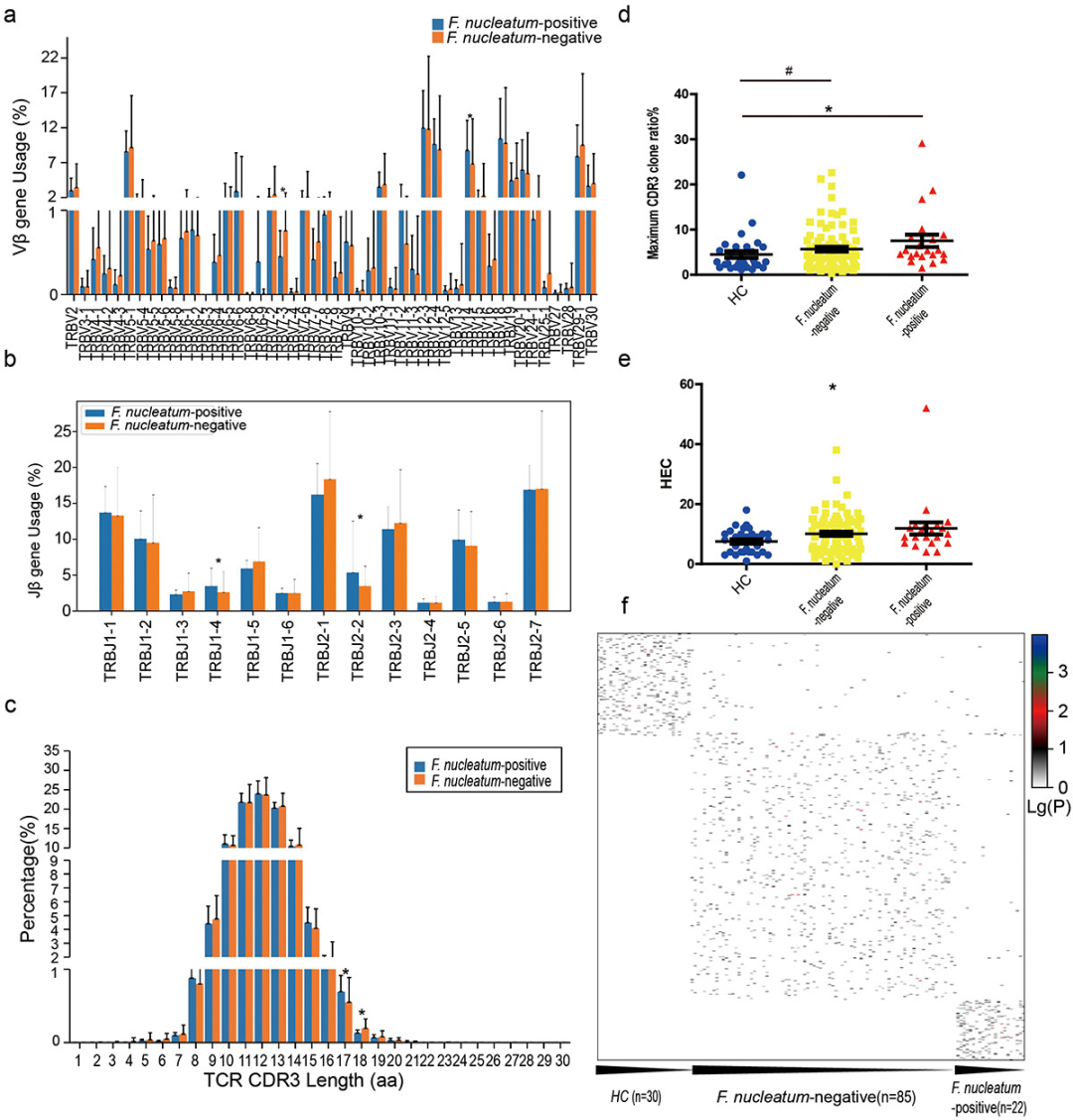
**6、核胞梭菌阳性和核胞梭菌阴性结直肠癌患者外周血TCRβ表达谱的不同特征。**
(a) Vβ基因使用比较,X轴为功能性人TRBV等位基因。(b) Jβ基因使用比较。x轴为功能性人类TRBJ等位基因。(c) TCRβ CDR3氨基酸序列长度分布比较。Y轴为具有相应CDR3长度的TCRβ CDR3克隆类型的百分比。(d)健康对照、核核f菌阳性和核核f菌阴性结直肠癌患者最大CDR3克隆比分布比较。(e)健康对照、核核f菌阳性和核核f菌阴性结直肠癌患者HEC数量分布比较。(f)所有样品的CDR3序列热图。(注:图a、b、c、d、e、f由益安博助力绘制)
### 讨论与展望
在本研究中,结直肠癌患者(n=107)和健康供者(n=30)外周血中表达的TCRβ谱的不同特征。结直肠癌患者TCRβ大克隆数量增加,TCR多样性很低。宏基因组测序数据显示,CRC患者(n=97)与HC患者(n=30)相比,核梭杆菌、大肠杆菌和Dasheen花叶病毒的相对丰度一致升高。与HC(n=30)相比,CRC(n=97)中prausnitzii粪杆菌和Roseburia intestinal丰度减少。研究了结直肠癌靶基因(16个基因,n=79)体细胞突变与TCR克隆性和微生物生物标志物的相关性。重要的是,我们构建了一个基于微生物组和TCR库的随机森林分类器(包含15个特征),该分类器可作为筛查CRC患者的临床检测方法。我们还分析了F. nucleatum特异性TCR库的特征。总的来说,我们的大队列多组学数据旨在识别新的生物标志物,为CRC的检测和诊断提供临床决策,这可能具有病因和诊断意义。
*参考文献:1.https://pubmed.ncbi.nlm.nih.gov/37795995/*

